La resolución de genomas, en particular de plantas, es una tarea muy compleja y propensa a errores. Esto se debe a que hay varias copias de todos los cromosomas y son muy parecidos.
por la Universidad Heinrich-Heine de Duesseldorf
Un equipo de investigadores en bioinformática de la Universidad Heinrich Heine de Düsseldorf (HHU) ha desarrollado ahora una herramienta de software que permite la asignación precisa a las copias correctas, un proceso conocido como «escalonamiento». Presentan su desarrollo en la última edición en línea de la revista Genome Biology .
Los genomas de todas las formas de vida superiores se almacenan en el núcleo celular de los cromosomas . Los cromosomas están compuestos por hebras de la molécula de ADN. La información genética en sí está codificada en una secuencia de pares de bases adyacentes de las moléculas adenina (A), citosina (C), guanina (G) y timina (T).
Las diferentes especies tienen diferentes números de cromosomas; por ejemplo, los humanos tienen 23, mientras que las papas tienen 12 y el trigo tiene 7. Además, existen diferentes copias o ‘haplotipos’ de los cromosomas. Los humanos tienen dos copias, una de la madre y otra del padre, mientras que las papas tienen cuatro y el trigo incluso seis. Las especies con dos copias se denominan «diploides», mientras que las que tienen más de dos son «poliploides». Las copias son casi idénticas, siendo «casi» la palabra clave. Son las diferencias entre ellos las que determinan la variabilidad de los organismos dentro de una población.
Para desbloquear la información genética, los investigadores abordaron algo parecido a un gran rompecabezas: tomaron una mayor cantidad de células, dividieron los genomas de las células en muchas partes pequeñas, llamadas ‘lecturas’, y secuenciaron la información contenida en esas partes. . Esto era necesario porque la tecnología actualmente disponible solo puede procesar pequeñas secciones de ADN.
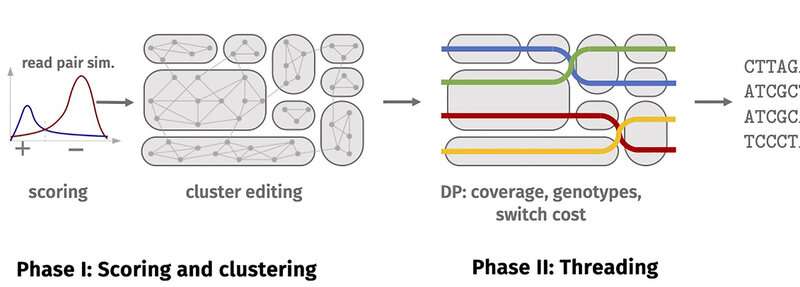
El resultado fue un enorme volumen de datos: miles de millones de lecturas, con un volumen de datos de varios cientos de gigabytes. Comprenden secuencias de diferentes longitudes compuestas por las letras A, C, G y T. La siguiente tarea de los investigadores de bioinformática fue determinar su posición dentro de un cromosoma, luego asignar las secciones correspondientes a un cromosoma (un proceso conocido como ‘mapeo ‘) y finalmente encontrar las copias correctas del cromosoma. Esta última etapa se conoce como «escalonamiento». La tarea se complica por los errores de secuenciación.
Hay herramientas buenas y eficientes disponibles para el mapeo. Sin embargo, las herramientas bioinformáticas necesarias para la eliminación gradual aún están en su infancia. Aquí fue precisamente donde el equipo de investigadores en bioinformática de HHU centró su atención. En un proyecto conjunto financiado por la Fundación Alemana de Investigación y gestionado por el Prof.Dr. Gunnar Klau (grupo de trabajo de Bioinformática Algorítmica) y el Prof.Dr. Tobias Marschall (Instituto de Biometría Médica y Bioinformática, Hospital Universitario de Düsseldorf) en colaboración con el Prof.Dr. Björn Usadel (Instituto de Ciencia de Datos Biológicos), desarrollaron una herramienta de software llamada ‘WhatsHap polifase’ y probaron la herramienta con éxito utilizando datos de modelos y el genoma de la papa .
Esta nueva herramienta resuelve el problema mediante un proceso de dos fases. La primera fase implica agrupar las lecturas, es decir, dividirlas en grupos. Las lecturas de un grupo probablemente provienen de un haplotipo o de una región de haplotipos idénticos. La segunda fase implica «enhebrar» los haplotipos a través de los grupos. Durante el enhebrado, las lecturas se asignan a los haplotipos de la manera más uniforme posible, lo que garantiza el menor salto posible de un grupo a otro.
La nueva herramienta se ha agregado al paquete principal ‘WhatsHap’, que está disponible gratuitamente. El paquete ya se ha utilizado para llevar a cabo con éxito la fase de conjuntos de cromosomas diploides, por ejemplo, para seres humanos. Esta nueva incorporación del equipo con sede en Düsseldorf significa que la eliminación gradual ahora también es posible para los organismos poliploides. El profesor Klau dijo: «Nuestra nueva tecnología permite que los genomas de las plantas se modifiquen por fases en alta resolución y con un bajo margen de error».
